Etchevers:Research
|
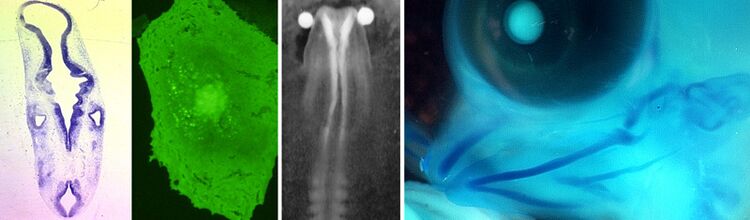
Thirty-second blurb for those who don't want to slog their way through the official summaries in French and English below. We want to understand what goes on within the cells that make up tissues subject to birth defects. Since there are more birth defects possible than tissues in the body, we are concentrating on a particular lineage that comes from cells appearing around the third week of pregnancy. These are called neural crest cells. They end up being part of the heart, most of the face, the front part of the eye, nearly all pigmented cells of the body, and the whole peripheral nervous system, among other things. So we study genetic defects that affect neural crest development, and thereby lead to malformations in those different progeny. Human neural crest cell differentiationOur current project concerns the transcriptional and phenotypic characterization of highly multipotent neural crest cells (NCC) derived from human embryos. Such characterization is a prerequisite to developing cell-based replacement therapies for congenital malformations or progressive diseases in which neural crest-derived lineages play a primary pathogenic role (“neurocristopathies”). A quantitative SAGE analysis of the entire set of mRNA transcripts derived from primary human NCC has been completed in our laboratory, in order to establish the transcriptional profile of genes that distinguish the undifferentiated state for this cell type. The SAGE data is being supplemented with that from a different functional genomics tool that is being exploited in our parent research group in the INSERM U781 and with our collaborators at Institut Curie, Affymetrix DNA microarrays. Statistical analysis and comparison of the SAGE and microarray results using bioinformatics allows us to class transcripts into functional clusters and identify groups of genes that are up- or down-regulated during NCC differentiation. In order to rapidly assess gene function, our group looks at the expression of candidate genes for certain neurocristopathies during normal human embryonic development using in situ hybridization on sections. We can also test the effects of gain or loss of gene function by targeting the NCC of the chicken embryo (a model with many technical advantages) using electroporation, and performing short- and long-term analyses. Over the long term, our group also plans to immortalize human NCC shortly after their initial migration, when they most resemble “true” stem cells in their potential. We will test the capacity of the cells to differentiate appropriately after transplantation in vivo into the developing chicken embryo. In this way, we can define the capacity of multipotent NCC to acquire diverse cell phenotypes in an appropriate environment. Our group is particularly interested in neurocristopathies of the cephalic pole, including eye malformations of the anterior chamber, congenital heart defects, and in the congenital giant naevus. Différenciation de la crête neurale humaineNotre projet concerne la caractérisation transcriptionnelle et phénotypique des cellules multipotentes de la crête neurale (CN) dérivée d’embryons humains. Cette recherche est indispensable avant d’envisager de développer des cytothérapies de remplacement pour des « neurocristopathies » congénitales ou progressives tels le syndrome de Hirschsprung ou certaines neuropathies périphériques. Nous entreprenons d’immortaliser des lignées de CN humaine peu de temps après la migration initiale de ces cellules, quand ils ont le plus grand potentiel de différenciation. Nous allons tester la capacité des lignées de se différencier correctement in vivo chez l’embryon de poulet. Une analyse quantitative SAGE du transcriptome entier des cellules CN humaines vient de terminer, afin d’établir le profil des gènes qui caractérisent l’état indifférencié de la CN. Enfin, nous corroborons ces résultats avec un autre outil de génomique fonctionnel, des puces Affymetrix, utilisés par les collaborateurs de l’équipe 2 de l’INSERM U781 et à l’Institut Curie. Nous comparons par exemple le profil transcriptionnel des ganglions fœtaux avec celui de leurs précurseurs multipotents. Une analyse statistique et une comparaison bio-informatique des résultats SAGE et microarray nous permet de classer les transcrits par groupes fonctionnels qui sont modulés au cours de la différenciation. Afin d’évaluer rapidement la fonction de tels groupes, nous examinons l’expression de gènes candidats pour des neurocristopathies humaines par l’hybridation in situ sur des coupes d’embryons humains normaux. Nous effectons aussi des gains ou pertes de fonction de ces gènes au sein de la CN de l’embryon de poulet afin de voir l’effet sur sa différenciation dans un environnement approprié. Ainsi, nous espérons identifier des nouveaux gènes responsables de neurocristopathies ainsi que de connaître leurs modes de fonctionnement qui pourront mener à des voies thérapeutiques. Le groupe s'intéresse particulièrement aux malformations congénitales qui touchent le pole céphalique, le coeur, la chambre antérieure de l'oeil et la peau. |